|
UTILIZACIÓN DE LAS ESTERASAS COMO MARCADORES GENÉTICOS EN
LAS POBLACIONES DE TILAPIAS Oreochromis mossambicus y O. urolepis hornorum
CULTIVADAS EN EL ESTADO DE MORELOS
Trabajo recibido el 16 de enero de 1992
y aceptado para su publicación el 6 de octubre de 1992 (La
redacción es responsabilidad de los autores).
USE OF THE ESTERASES AS GENETIC MARKERS IN THE TILAPIAS Oreochromis mossambicus y O. urolepis hornorum RAISED IN THE STATE OF MORELOS, MEXICO
Píndaro Díaz-Jaimes y Manuel Uribe-Alcocer
Laboratorio de Genética de
Organismos Acuáticos, Instituto de Ciencias del Mar y Limnología,
Universidad Nacional Autónoma de México. Apartado Postal 70-305,
México, D.F. 04510, MÉXICO. Contribución No. 729 del
Instituto de Ciencias del Mar y Limnología.
A fin de evaluar la
posibilidad de determinar a través de marcadores genéticos el
grado de pureza del linaje de los lotes de reproductores de
Oreochromis mossambicus y O. urolepis
hornorum utilizados en la producción de progenie monosexual
masculina en las piscifactorías de México, se realizó el
estudio electroforético de las esterasas presentes en el
mucus superficial de especímenes provenientes de dos
centros piscícolas del estado de Morelos. Se detectaron tres loci, dos
de los cuales fueron polimórficos EST-1 (100/108) y
EST-3 (100/55) en ambas especies. Las frecuencias
genotípicas del locus Est-1 en
O. mossambicus difieren de las del equilibrio de
Hardy-Weinberg, posiblemente debido a procesos endogámicos resultantes
del manejo de esta población. La estructura genética actual de
las poblaciones estudiadas no permite la identificación
inequívoca de los especimenes, aunque permite formular la
recomendación de que los alelos Est-1 (100) y
Est-3 (100) sean incorporados como marcadores
genéticos específicos a los reproductores de O.
mossambicus, mientras que los alelos
complementarios Est-1 (108) y Est-3 (55)
lo sean a los de O. u. hornorum.
An
electrophoretic survey of two fish factories of the state of Morelos,
México, was undertaken to assess the possibility of using these loci as
genetic markers for the broodstock of Oreochromis
mossambicus and O. urolepis hornorum, used widely
in the fish factories of Mexico to produce hybrid male monosexual offspring.
Three loci were detected, two of which, EST-1 (100/108) and
EST-3 (100/55), were polymorphic in both species. The
genotypic frequencies found in the locus Est-1 in
O. mossambicus did not agree with the Hardy - Weinberg
equilibrium, possibly due to endogamic processes in the management of this
population. The genetic structure found in the samples does not allow
inequivocal identification of individual broodstock fishes, although it allows
to recommend that loci Est-1 (100) and
Est-3 (100), be incorporated as species-specific genetic
indicators to the broodstock of O. mossambicus, while the
loci Est-1 (108) and Est-3 (55) be
icorporated to O. u. homorum.
La acuicultura en México ha adquirido gran importancia como una alternativa de producción alimentaria y de generación de divisas. La identificación de las poblaciones de peces utilizadas, así como la selección de las líneas genéticas adecuadas (Moav et al., 1976), son esenciales para el mantenimiento y mejoramiento de las características deseables en términos de calidad y producción. Las tilapias son peces endémicos de África que han sido introducidos con fines de cultivo en diferentes regiones tropicales (Camacho et al.,1984). Las especies Tilapia mossambica (Oreochromis mossambicus), T nilotica (Oreochromis niloticus) y T. melanopleura (T. zilii), destinadas a la producción de híbridos, fueron introducidas a México en 1964, procedentes de Auburn, Alabama (Rosas, 1976). En gran parte de las piscifactorías mexicanas se ha utilizado la cruza entre las líneas de Oreochromis mossambicus albinas y O. urolepis hornorum para producir progenie monosexual masculina que tiene un mayor potencial de crecimiento y rendimiento (Hickling, 1960; Majumdar y McAndrew, 1983). Sin embargo, debido a la complejidad en el monitoreo de los lotes de reproductores y por la gran semejanza de la pigmentación entre la línea albina parental de O. mossambicus y la de algunos de los híbridos, y por otras causas (FAO, PNUMA, 1984), posiblemente se hayan incorporado algunos de éstos a las líneas parentales, dando como resultado pérdida de su potencial de producción de progenie monosexual. Esto ha resultado en híbridos de ambos sexos que se cruzan entre sí con fertilidad precoz produciendo gran cantidad de peces pequeños sin importancia económica (Avtalion, 1982). A fin de evitar esta situación desventajosa, es importante realizar una evaluación permanente de las líneas utilizadas como progenitoras de lotes híbridos, a fin de probar su grado de pureza, a través de la utilización de marcadores genéticos que faciliten la exclusión de los hibridos de los lotes de reproductores. Se han realizado varios estudios enfocados a la búsqueda de marcadores genéticos en diferentes especies de tilapias a partir de técnicas electroforéticas y citogenéticas, para lograr la identificación precisa de las líneas reproductoras (Avtalion, 1982; Herzberg, 1978; Chen y Tsuyuki, 1970; Majumdar y McAndrew, 1986; McAndrew y Majumbar 1983; UribeAlcocer y Arreguín, 1989; Avtalion et al., 1975; Camacho et al., 1984 y Uribe-Alcocer et al., 1989). Sin embargo, se requiere de una técnica que permita mantener vivo al pez, causándole el menor daño posible, de modo que se puedan conservar los organismos deseables dentro de los lotes de reproductores. El objetivo de este estudio fue analizar las esterasas presentes en el mucus superficial de las poblaciones de tilapia utilizadas como lotes de reproductores en las piscifactorías del estado de Morelos, así como de sus híbridos, a fin de evaluar su posible utilización como marcadores genéticos en el manejo de estas poblaciones. MATERIAL Y MÉTODOSSe tomaron muestras del lote de reproductores de Oreochromis mossambicus y O. urolepis hornorum del Centro de producción piscícola ubicado en Zacatepec, Morales. También fueron analizadas muestras de híbridos F1 O. mossambicus x O. u. hornorum, provenientes de la Piscifactoría "El Rodeo", ubicada en el mismo estado. Se estudiaron 75 muestras, de las cuales 30 correspondieron a O. mossambicus, 30 a O. u. hornorum y 15 a los organismos híbridos (Díaz-Jaimes, 1987). Las muestras fueron tomadas del mucus superficial del pez, utilizando algodón esterilizado, y difundidas en una solución de Trizma 0.001 M. (Herzberg, 1978). Se centrifugaron a 15,000 rpm durante 10 minutos y se colocaron en tubos de vidrio etiquetados. Se congelaron durante 24 horas a - 4ºC antes de ser procesadas por electrofóresis. Se utilizaron geles de poliacrilamida en un equipo de electrofóresis horizontal (LKB 82117), con un sistema discontinuo de amortiguadores (Tris-HCl, pH 8.1 para el ánodo y Tris-glicina, pH 8.9, para el cátodo) durante una hora a 400 mA y 220 volts. La tinción histoquítrúca se llevo a cabo utilizando como sustrato alfa y beta naftil-acetato y azul rápido para la detección de la actividad enzimática de las esterasas. Los loci detectados fueron nombrados siguiendo los criterios de Allendorf y Utter (1979). A fin de poder derivar la distancia taxonómica promedio (DTP) (Sokal, 1961), se elaboró la matriz de datos siguiendo la metodología de Crisci y López-Armengol (1985), a partir de las frecuencias alélicas de los loci polimórficos detectados. RESULTADOS Y DISCUSIÓNLos patrones electroforéticos de las esterasas provenientes del mucus superficial de estos organismos mostraron la presencia de tres loci (Fig. 1), dos de los cuales presentaron polimorfismo y se han designado como EST-1 (100/108) y EST-3 (100/55). El locus EST-2 fue monomórfico. Estos loci presentan patrones de estructura monomérica. 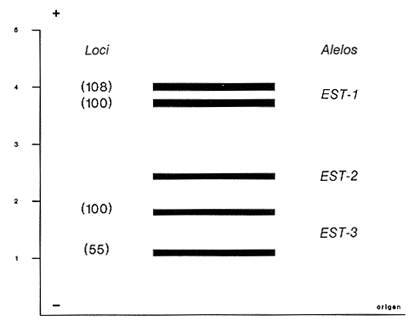 Figura 1. Patrón electroforético en gel de poliacrilamida de las esterasas en las poblaciones de Oreochromis urolepis hornorum y O. mossambicus ( 1 hora a 400 mA y 222 volts). Resultados similares han sido obtenidos por diversos autores que han analizado las esterasas en distintas especies de tilapias. Chen y Tsuyuki (1970) describieron la presencia de un locus en las esterasas provenientes del plasma sanguíneo de Tilapia hornorum (Oreochromis urolepis hornorum) y T mossambica (O. mossambicus), con alelos diferentes fijados en cada una de las dos especies, y ambos presentes en el híbrido. Herzberg, en 1978, informó del hallazgo de tres loci en las esterasas del mucus superficial de Tilapía mossambica (Oreochromis mossambicus), dos de las cuales, a juzgar por las ilustraciones presentadas en su publicación, presentaron polimorfismo, genético, mientras que Avtalion (1982) no reporta diferencias en las esterasas del plasma sanguíneo de Sarotherodon mossambicus (Oreochromis mossambicus) y de S. hornorum (O. urolepis hornorum). 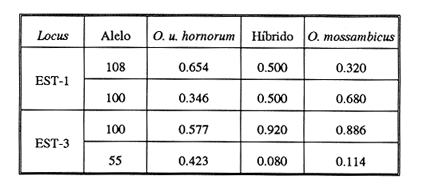 TABLA 1. Distribución de las frecuencias alélicas de los loci polimórficos en las poblaciones de Oreochromis urolepis hornorum, O.mossambicus y los híbridos McAndrew y Majumdar (1983) detectaron dos loci fijados, de estructura monomérica, en las esterasas de suero de músculo en ejemplares de Sarotherodon mossambicus (O. mossambicus) procedentes de Mozambique. La distribución de las frecuencias alélicas del locus EST-1 (100/108), mostró una clara diferenciación interespecífica representada por una mayor frecuencia del alelo EST-1 (108) en la población de Oreochromis urolepis hornorum, mientras que en O. mossambicus se encontró una frecuencia mayor del alelo EST-1 (100) [Tabla 1], detectado principalmente en estado homócigo. En contraste, el alelo EST-3 (55) en esta última especie se encuentra únicamente formando parte de genotipos heterocigotos. Por otra parte en O. urolepis hornorum, se detectó una frecuencia mayor del alelo EST-3 (100) que de su alelo complementario EST-3 (55) ambos presentes principalmente en genotipos heterocigotos, y en equilibrio de Hardy-Weinberg. 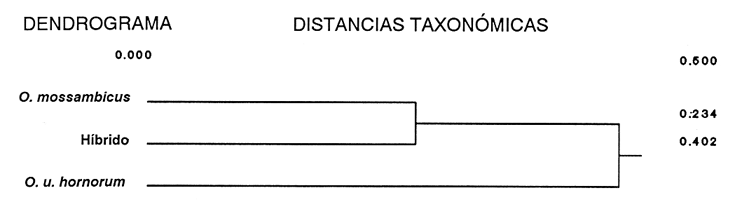 Figura 2. Dendrograma obtenido a partir de las frecuencias alélicas de los loci polimórficos, que enfatiza la proximidad genética entre el híbrido y Oreochromis mossambicus 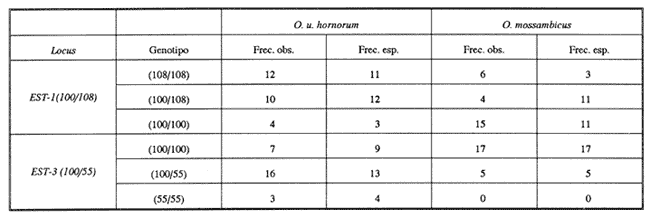 TABLA 2 Frecuencias genotípicas observadas y esperadas de las poblaciones estudiadas, de acuerdo con la distribución de Hardy-Weinberg. La distribución de las frecuencias genotípicas (Tabla 2), correspondió con el equilibrio de Hardy-Weinberg en los loci que resultaron polimórficos de Orechromis urolepis hornorum y en el locus EST-3 (100/55) de O. mossambicus. En contraste, el locus EST-1 de esta última, en el cual las diferencias entre las frecuencias observadas y esperadas fueron significativas (X²= 8.9, p > 0.05, 1 gl), se observa una deficiencia de genotipos heterocigotos, que posiblemente sea el resultado de procesos endogámicos que hayan favorecido la homocigosis. A fin de comprobar la diferenciación poblacional de las muestras estudiadas, así como para evaluar el grado de proximidad de sus genotipos, se elaboró el dendrograma que se muestra en la figura 2. Fue obtenido a partir de la matriz de datos que aparecen en la tabla 1, y pone en evidencia una clara separación en la distribución de las frecuencias alélicas entre las poblaciones de tilapia analizadas, con una distancia taxonómica que muestra un porcentaje de similitud del 74.2% entre el híbrido y O. mossambicus (DTP=0.129), que a su vez se separan de O. u. hornorum por una DTP =0.329 (46.8 % de similitud). Así mismo, el índice de Wright (Allendor y Phelps, 1986) obtenido de las diferencias alélicas encontradas en las esterasas fue de F st =0.1409, confirmando la diferenciación genética presente entre las poblaciones estudiadas. Resultados similares han sido obtenidos por McAndrew y Majumdar (1983), quienes reportaron un índice de heterocigocidad promedio bajo para Oreochromis mossambicus, propiciado probablemente también por la endogamia debida a la manipulación selectiva de la población estudiada para la obtención de líneas albinas con fines de cultivo en la producción de híbridos. En Oreochromis urolepis hornorum, los valores del índice de heterocigocidad por loci (h) [Nei y Roychoudhury 1974], mostraron valores altos (h-0.4572 en la EST-1 y h=0.5078 en la EST-3) y las diferencias entre las frecuencias observadas y esperadas de acuerdo al equilibrio de Hardy Weinberg no fueron significativas debido probablemente a procesos de reproducción abierta, si no panmíctica, presentes en O. u. hornorum al tratarse de poblaciones que han sido menos manipuladas genéticamente. Los resultados de los estudios realizados por McAndrew y Majumdar (1983) en organismos de S. mossambicus (O. mossambicus), difieren parcialmente de los del presente estudio, ya que ellos informan haber detectado únicamente dos loci monoméricos fijados en las esterasas de esta especie. Las diferencias pueden deberse a las técnicas seguidas, a los tejidos utilizados, o a que en la población examinada por los autores mencionados no se encuentren los alelos presentes en las poblaciones estudiadas debido a eventos de: a) deriva génica, b) de endogamia por ser cepas procedentes de establecimientos comerciales, o bien, lo que se considera más probable, c) que correspondan a la constitución genética original de las poblaciones de O. mossambicus. Si éste es el caso, implicaría que, las poblaciones presentes en el estado de Morelos, utilizadas como reproductores en las cruzas híbridas, han sufrido cierto grado de mezcla genética al paso del tiempo. Lo anterior, permite considerar que en Oreochromis mossambicus, los alelos EST-1(100) y EST-3(100) hayan sido los alelos originales, a juzgar por su elevada frecuencia en la muestra estudiada y por los resultados obtenidos en otros estudios (McAndrew y Majumdar, 1983), y asumimos que los alelos complementarios EST-1(108) y EST-3(55) hayan sido los correspondientes a O. urolepis hornorum. La distribución de las frecuencias génicas de los alelos polimórficos detectados en las poblaciones estudiadas, tanto de O. urolepis hornorum como de O. mossambicus, no permite utilizar actualmente estos rasgos genéticos en la identificación específica de sus reproductores a nivel individual, ya que no permiten una discriminación inequívoca entre ellos ni entre sus híbridos. RECOMENDACIONESComo resultado de este estudio se sugiere que, en primera instancia, en los trabajos de selección y mejoramiento de los lotes de reproductores, se incorporen exclusivamente organismos de Oreochromis mossambicus portadores homocigóticos de los genes EST-1 (100) y EST-3 (100), que se considera corresponden a los alelos originales de esta especie, y, al mismo tiempo, que los organismos de O. urolepis hornorum incorporados sean portadores de los loci EST-1 (108) y EST-3 (55). Igualmente sería conveniente su complementación con la incorporación de variantes electroforéticas específicas detectadas en otras proteínas, como la hemoglobina (Camacho et al., 1984; Uribe-Alcocer et al., 1989). De esta manera será posible verificar, a nivel individual y sin perjuicio de los especímenes, la pureza de la línea, a fin de mantener el potencial de progenie monosexual masculina, resultante de la cruza híbrida entre las especies estudiadas, y el mejoramiento de la producción acuícola. El esquema de cruza interespecífica Oreochromis mossambicus x O. urolepis hornorum para la obtención de progenie monosexual masculina es uno de los más extensamente utilizados en las piscifactorías de México, por lo que los resultados de esta investigación pueden ser de utilidad en el manejo de varios de los sistemas de acuicultura del país. AgradecimientosEste trabajo fue realizado con fondos del presupuesto interno otorgado por la UNAM al Instituto de Ciencias del Mar y Limnología, así como con fondos proporcionados por el CONACyT al proyecto PCCBBNA-021431: "Estudios genéticos en peces de importancia alimentaria y económica a) Género Tilapia. b) Género Dormitator." Se agradece la donación de los especímenes estudiados a la Delegación Federal de Pesca del Estado de Morelos, a la Bióloga Isabel Cadena Uchida su apoyo para el presente estudio. Se agradece igualmente la colaboración técnica del Biólogo Ángel Ramírez Escamilla y de la Bióloga Yolanda Hornelas Orozco. LITERATURAALLENDORF, F. W., and S. R. PHELPS Use of allelic frequencies to describe population structure. Can. J. Fish. Aquat. Sci., 1981 1507-1514 38 ALLENDORF, F. W., and F. M. UTTER Fish Physiology, Population Genetics. In: W.S. HOAR, D.J. Randall y J.R. Brett (Eds.). Academic Press, New York, 1979 417-454 8 AVTALION, R. R., Y. PRUGININ, and S. ROTHBARD, Bamidgeh Determination of allogeneic and xenogeneic markers in the genus of Tilapia: I. Identification of sex and hybrids in Tilapia by electrophoretic analysis of serum proteins. 1975 8-13 27 1 AVTALION, R. R The biology and culture of Tilapias. Genetic markers in Sarotherodon and their use for sex and species identification. In: R.S.V. Pullin, and R.H. LoweMcConnell (Eds.). ICLARM Conference Proceedings 7. Internacional Center for Living Resources Management, Manila, Philippines 1982 432- 442 CAMACHO, A., V. RIVALTIA, A. VILLAESCUSA, and R. CABALLERO Ciencias Biológicas Las isoenzimas en el estudio de Tilapia y géneros afines existentes en Cuba. I. Características electroforéticas de seis sistemas proteínicos. 1984 11-22 12 CHEN, F. Y., and H. TSUYUKI, J. Fish. Res. Bd. Canada, Zone electrophoretic studies on the protein of Tilapia mossambica and T. hornorum and their F1 hybrids, T. zillii and T. melanopleura. 1970 2167-2177 27 CRISCI, J. V., y M. F. LÓPEZ-ARMENGOL, Programa Regional de Desarrollo Científico y Tecnológico. Introducción a la teoría y práctica de la taxonomía numérica Secretaría General de la OEA. Wash. D.C 1983 132 DÍAZ-JAIMES, P., Tesis Profesional. Estudio electroforético de las esterasas en las poblaciones de tilapia sujetas a explotación en el estado de Morelos. Facultad de Ciencias, UNAM. 1987 55 FAO/PNUMA Doc. Técn. Pesca Conservación de los recursos genéticos de los peces. Problemas y recomendaciones. Informe de la Consulta de Expertos sobre los recursos genéticos de los peces. FAO. 1984 42 217 HERZBERG, A., Aquaculture, Electrophoretic esterase patterns of the surface mucus for the identification of Tilapia species. 1978 81-83 13 HICKLING, C. F., J. Genet., The Malacca tilapia hiybrids. 1960 1-10 57 MAJUMDAR, K. C and B. J. MCANDREW International Symposium on Tilapia aquaculture. Sex ratios from interespecific crosses within the tilapias. In: L. Fishelson y Z. Yaron (Eds.). Nazareth, Israel, 1983 261-269 MCANDREW, B. J., and K. C. MAJUMDAR Aquaculture, Tilapia stock identification using electrophoretic markers. 1983 249-261 30 MOAV, R., T. B. BRODY, G. WHOLFARTH, y G. HULATA, Aquaculture, Applications of electrophoretic genetic markers to fish breeding. I. Advantages and methods. 1976 217-228 9 NEI, M., y A. K. ROYCHOUDHURY Genetics Sampling variances of hetero-zygosity and genetic distace. 1974 379-390 76 ROSAS, M. M., Peces dulceacuícolas que se explotan en México y datos sobre su cultivo. Inst. Nal. de Pesca. Centro de Estudios Económicos y Sociales del Tercer Mundo, A.C., 1976 75-85 SOKAL, R. R., Syst. Zool., Distance as a measure of taxonomic similarity. 1961 40-51 10 70 URIBE-ALCOCER, M., y J. ARREGUÍN-ESPINOSA An. Inst. Cienc. del Mar y Limnol. Los cromosomas de los peces Oreochromis urolepis hornorum y Oreochromis mossambicus (Pisces: Cichilidae). Univ. Nal. Autón. México, 1989 189-198 16 2 URIBE-ALCOCER, M., G. VERA-MUÑOZ, y J. ARREGUÍN-EPINOSA An. Inst. Cienc. del Mar y Limnol. Marcadores electroforéticos específicos de Oreochromis mossambicus y Oreochromis urolepis hornorum (Pisces: Ciclilidae). Univ. Nal. Autón México, 1989 199-206 16
|

